2D color gradient
对于热图大家都熟悉,热图中的颜色表示值的大小。但前几天看到一个热图,里面的颜色含有两个维度的信息,专门有一个颜色的图注(非主图,而是热图里面的颜色说明),如下,横坐标表示D值的大小,纵坐标表示的P值,可以看出二维区域中不同位置的颜色,同时反应了D值和P值的信息。

找了很多工具和方法,都不太方便实现,或者不太容易控制颜色的分布。后来突然悟了,我可以自己生成这个图,从左到右反应的D值大小,两个颜色渐变,从上往下反应的是P值显著性,颜色越来越深。

对于热图大家都熟悉,热图中的颜色表示值的大小。但前几天看到一个热图,里面的颜色含有两个维度的信息,专门有一个颜色的图注(非主图,而是热图里面的颜色说明),如下,横坐标表示D值的大小,纵坐标表示的P值,可以看出二维区域中不同位置的颜色,同时反应了D值和P值的信息。

找了很多工具和方法,都不太方便实现,或者不太容易控制颜色的分布。后来突然悟了,我可以自己生成这个图,从左到右反应的D值大小,两个颜色渐变,从上往下反应的是P值显著性,颜色越来越深。
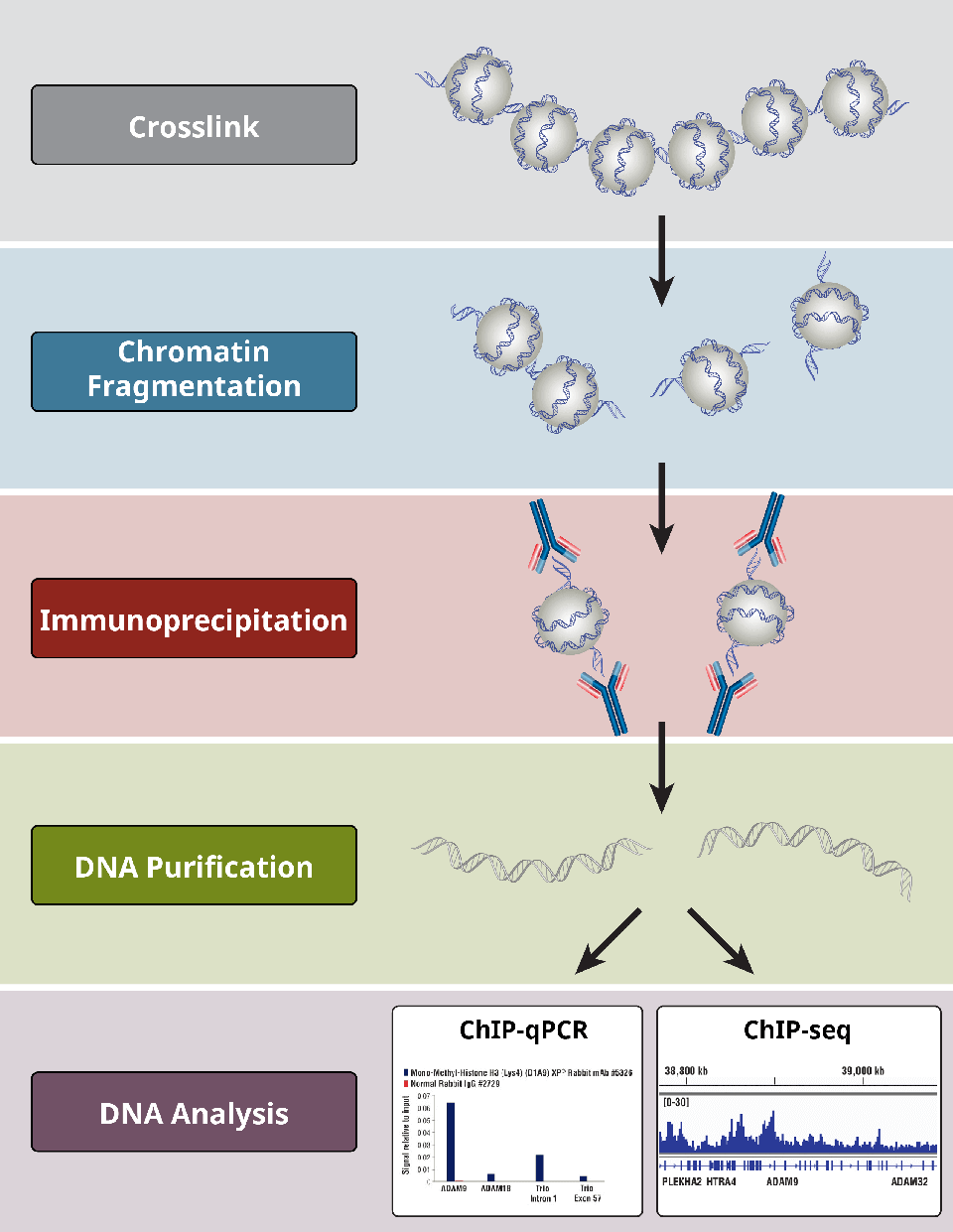
染色质免疫共沉淀(Chromatin Immunoprecipitation,ChIP)与二代测序相结合的表观遗传研究技术,能够高效地在全基因组范围内对DNA和蛋白的相互作用进行检测,通常用于转录因子结合位点或组蛋白特异性修饰位点的研究。
染色质免疫沉淀法 (ChIP) 是一种基于抗体的技术,可用来选择性地使特异性 DNA 结合蛋白及其 DNA 靶标富集。ChIP 可用来研究某种特殊的蛋白-DNA 相互作用、多种蛋白-DNA 相互作用或全基因组或部分基因内的相互作用。
ChIP 使用可选择性地检测和结合蛋白的抗体,包括组蛋白、组蛋白修饰、转录因子、辅因子,以提供有关染色质状态和基因转录的信息。在 ChIP 中结合使用蛋白质组分析和分子生物学技术,能够让研究者理解目的细胞或组织中的基因表达和调节。
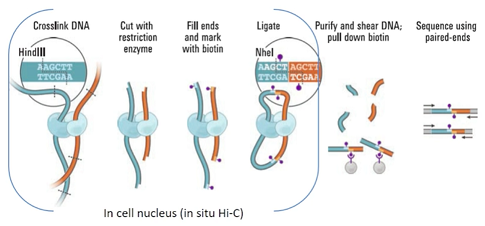
Hi-C技术源于染色体构象捕获(Chromosome Conformation Capture, 3C)技术,利用高通量测序技术,结合生物信息分析方法,研究全基因组范围内整个染色质DNA在空间位置上的关系,获得高分辨率的染色质三维结构信息。Hi-C技术不仅可以研究染色体片段之间的相互作用,建立基因组折叠模型,还可以应用于基因组组装、单体型图谱构建、辅助宏基因组组装等,并可以与RNA-Seq、ChIP-Seq等数据进行联合分析,从基因调控网络和表观遗传网络来阐述生物体性状形成的相关机制。
我用bowtie比对了序列,想查看reads的错配情况。SAM flag中的M包含了比对上的碱基和错位的碱基,不能区分错配。
参考bowtie的文档,可以看到XM的标签可以指示mismatch的个数,MD标签可以查看具体的错配情况。
XN:i:<N> |
The number of ambiguous bases in the reference covering this alignment. Only present if SAM record is for an aligned read. |
XM:i:<N> |
The number of mismatches in the alignment. Only present if SAM record is for an aligned read. |
MD:Z:<S> |
A string representation of the mismatched reference bases in the alignment. See SAM Tags format specification for details. Only present if SAM record is for an aligned read. |
SAM手册对与MD的介绍
|
|
Single-cell transcriptomic analysis highlights origin and pathological process of human endometrioid endometrial carcinoma
https://www.nature.com/articles/s41467-022-33982-7
子宫内膜癌(Endometrial cancer, EC)是妇科最常见的恶性肿瘤之一,子宫内膜样子宫内膜癌(endometrioid endomecancer, EEC)是EC的主要病理类型。
在雌激素依赖性EEC肿瘤发生过程中,子宫内膜在没有孕激素保护的情况下长期暴露于雌激素中,表现出不受控制的增殖,并且可以从正常子宫内膜发展到非典型子宫内膜增生(AEH, EEC癌前阶段),然后逐步发展到EEC。关于ECC的起源过往研究推测包括子宫内膜上皮和基质干成分在内的多种谱系可能是EEC的起源,但证据不足以支持明确起源。
肿瘤微环境由免疫细胞、成纤维细胞、周细胞等组成,在肿瘤的发生、预后和转移中起重要作用,尽管先前的研究已经提示肿瘤微环境在预后和治疗耐药的潜在作用,但从正常子宫内膜到EEC形成的过程仍不明确。
|
|